plotfig 1.5.0__tar.gz → 1.6.0__tar.gz
This diff represents the content of publicly available package versions that have been released to one of the supported registries. The information contained in this diff is provided for informational purposes only and reflects changes between package versions as they appear in their respective public registries.
- {plotfig-1.5.0 → plotfig-1.6.0}/.github/workflows/website_deploy.yml +1 -1
- {plotfig-1.5.0 → plotfig-1.6.0}/.gitignore +2 -9
- plotfig-1.6.0/.release-please-manifest.json +1 -0
- plotfig-1.6.0/CHANGELOG.md +147 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/PKG-INFO +44 -53
- {plotfig-1.5.0 → plotfig-1.6.0}/README.md +35 -46
- plotfig-1.6.0/docs/api/index.md +20 -0
- plotfig-1.6.0/docs/changelog.md +4 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/index.md +5 -8
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/installation.md +11 -15
- plotfig-1.6.0/docs/usage/brain_surface_files/brain_surface_5_0.png +0 -0
- plotfig-1.6.0/docs/usage/brain_surface_files/brain_surface_6_0.png +0 -0
- plotfig-1.6.0/docs/usage/brain_surface_files/brain_surface_9_0.png +0 -0
- plotfig-1.6.0/docs/usage/circos.md +216 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_11_0.png +0 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_13_1.png +0 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_1_0.png +0 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_3_0.png +0 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_5_0.png +0 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_7_0.png +0 -0
- plotfig-1.6.0/docs/usage/circos_files/circos_9_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/correlation.md +3 -4
- plotfig-1.6.0/docs/usage/correlation_files/correlation_4_0.png +0 -0
- plotfig-1.6.0/docs/usage/correlation_files/correlation_7_0.png +0 -0
- plotfig-1.6.0/docs/usage/correlation_files/correlation_9_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/matrix.md +2 -3
- plotfig-1.6.0/docs/usage/matrix_files/matrix_4_0.png +0 -0
- plotfig-1.6.0/docs/usage/matrix_files/matrix_7_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/multi_groups.md +3 -3
- plotfig-1.6.0/docs/usage/multi_groups_files/multi_groups_3_0.png +0 -0
- plotfig-1.6.0/docs/usage/multi_groups_files/multi_groups_6_0.png +0 -0
- plotfig-1.6.0/docs/usage/multi_groups_files/multi_groups_9_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group.md +41 -43
- plotfig-1.6.0/docs/usage/single_group_files/single_group_12_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_14_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_17_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_20_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_22_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_24_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_26_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_28_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_31_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_34_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_36_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_39_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_3_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_6_0.png +0 -0
- plotfig-1.6.0/docs/usage/single_group_files/single_group_8_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/mkdocs.yml +1 -2
- plotfig-1.6.0/notebooks/brain_connectivity.ipynb +99 -0
- plotfig-1.6.0/notebooks/brain_surface.ipynb +210 -0
- plotfig-1.6.0/notebooks/circos.ipynb +363 -0
- plotfig-1.6.0/notebooks/correlation.ipynb +218 -0
- plotfig-1.6.0/notebooks/matrix.ipynb +151 -0
- plotfig-1.6.0/notebooks/multi_groups.ipynb +227 -0
- plotfig-1.6.0/notebooks/single_group.ipynb +1008 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/pyproject.toml +12 -25
- plotfig-1.6.0/release-please-config.json +28 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/__init__.py +23 -20
- plotfig-1.6.0/src/plotfig/bar.py +1070 -0
- plotfig-1.6.0/src/plotfig/brain_connection.py +316 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/brain_surface.py +2 -9
- plotfig-1.6.0/src/plotfig/circos.py +233 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/correlation.py +11 -13
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/matrix.py +29 -33
- plotfig-1.6.0/src/plotfig/utils/__init__.py +11 -0
- plotfig-1.6.0/src/plotfig/utils/color.py +53 -0
- plotfig-1.6.0/src/plotfig/utils/matrix.py +59 -0
- plotfig-1.6.0/tests/test.ipynb +74 -0
- plotfig-1.6.0/tests/test.py +17 -0
- plotfig-1.6.0/uv.lock +2065 -0
- plotfig-1.5.0/.release-please-manifest.json +0 -3
- plotfig-1.5.0/CHANGELOG.md +0 -115
- plotfig-1.5.0/docs/api/index.md +0 -28
- plotfig-1.5.0/docs/usage/brain_surface_deprecated.md +0 -135
- plotfig-1.5.0/docs/usage/brain_surface_deprecated_files/brain_surface_deprecated_10_1.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_deprecated_files/brain_surface_deprecated_11_1.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_deprecated_files/brain_surface_deprecated_7_1.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_deprecated_files/brain_surface_deprecated_7_2.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_deprecated_files/brain_surface_deprecated_8_1.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_deprecated_files/brain_surface_deprecated_8_2.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_files/brain_surface_5_0.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_files/brain_surface_6_0.png +0 -0
- plotfig-1.5.0/docs/usage/brain_surface_files/brain_surface_9_0.png +0 -0
- plotfig-1.5.0/docs/usage/circos.md +0 -56
- plotfig-1.5.0/docs/usage/circos_files/circos_1_0.png +0 -0
- plotfig-1.5.0/docs/usage/circos_files/circos_1_1.png +0 -0
- plotfig-1.5.0/docs/usage/circos_files/circos_2_0.png +0 -0
- plotfig-1.5.0/docs/usage/correlation_files/correlation_4_0.png +0 -0
- plotfig-1.5.0/docs/usage/correlation_files/correlation_7_0.png +0 -0
- plotfig-1.5.0/docs/usage/correlation_files/correlation_9_0.png +0 -0
- plotfig-1.5.0/docs/usage/matrix_files/matrix_4_0.png +0 -0
- plotfig-1.5.0/docs/usage/matrix_files/matrix_7_0.png +0 -0
- plotfig-1.5.0/docs/usage/multi_groups_files/multi_groups_3_0.png +0 -0
- plotfig-1.5.0/docs/usage/multi_groups_files/multi_groups_6_0.png +0 -0
- plotfig-1.5.0/docs/usage/multi_groups_files/multi_groups_9_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_12_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_14_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_17_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_20_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_22_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_24_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_26_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_28_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_31_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_34_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_36_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_39_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_3_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_6_0.png +0 -0
- plotfig-1.5.0/docs/usage/single_group_files/single_group_8_0.png +0 -0
- plotfig-1.5.0/release-please-config.json +0 -10
- plotfig-1.5.0/src/plotfig/bar.py +0 -924
- plotfig-1.5.0/src/plotfig/brain_connection.py +0 -241
- plotfig-1.5.0/src/plotfig/brain_surface_deprecated.py +0 -1288
- plotfig-1.5.0/src/plotfig/circos.py +0 -287
- plotfig-1.5.0/uv.lock +0 -1795
- {plotfig-1.5.0 → plotfig-1.6.0}/.github/workflows/dependency_review.yml +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/.github/workflows/python_publish.yml +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/.github/workflows/release.yml +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/.github/workflows/summary_new_issues.yml +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/.github/workflows/sync_to_gitee.yml +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/.python-version +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/LICENSE +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/chimpanzee_bna.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/human_bna.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/human_glasser.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/macaque_bna.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/macaque_charm5.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/macaque_charm6.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/atlas_csv/macaque_d99.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/assets/plotfig.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_connectivity.md +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_connectivity_files/human.gif +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface.md +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_10_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_10_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_11_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_12_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_13_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_13_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_14_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_14_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_15_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_16_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_17_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_18_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_19_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_20_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_21_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_23_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_24_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_25_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_4_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_6_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_7_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_7_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_8_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_8_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/brain_surface_files/brain_surface_9_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/correlation_files/correlation_2_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/correlation_files/correlation_3_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/correlation_files/correlation_5_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/correlation_files/correlation_6_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/correlation_files/correlation_8_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/matrix_files/matrix_2_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/matrix_files/matrix_3_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/matrix_files/matrix_5_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/matrix_files/matrix_6_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/multi_groups_files/multi_groups_2_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/multi_groups_files/multi_groups_5_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/multi_groups_files/multi_groups_8_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_11_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_13_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_16_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_19_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_21_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_23_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_25_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_27_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_2_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_30_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_33_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_35_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_37_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_40_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_5_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_6_1.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/docs/usage/single_group_files/single_group_7_0.png +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/overrides/main.html +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/chimpanzee_bna.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/human_bna.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/human_glasser.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/macaque_bna.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/macaque_charm5.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/macaque_charm5_add_13_sgms.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/macaque_charm6.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/atlas_tables/macaque_d99.csv +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/chimpanzee_BNA/ChimpBNA.L.32k_fs_LR.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/chimpanzee_BNA/ChimpBNA.R.32k_fs_LR.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/human_BNA/fsaverage.L.BNA.32k_fs_LR.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/human_BNA/fsaverage.R.BNA.32k_fs_LR.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/human_Glasser/fsaverage.L.Glasser.32k_fs_LR.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/human_Glasser/fsaverage.R.Glasser.32k_fs_LR.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_BNA/MBNA_124_32k_L.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_BNA/MBNA_124_32k_R.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_CHARM5/L.charm5.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_CHARM5/R.charm5.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_CHARM6/L.charm6.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_CHARM6/R.charm6.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_D99/L.d99.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/atlases/macaque_D99/R.d99.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/chimpanzee_BNA/ChimpYerkes29_v1.2.L.midthickness.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/chimpanzee_BNA/ChimpYerkes29_v1.2.L.veryinflated.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/chimpanzee_BNA/ChimpYerkes29_v1.2.R.midthickness.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/chimpanzee_BNA/ChimpYerkes29_v1.2.R.veryinflated.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/README.md +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_desc-nomedialwall_dparc.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_desc-sulc_midthickness.shape.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_desc-vaavg_midthickness.shape.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_inflated.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_midthickness.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_sphere.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-L_veryinflated.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_desc-nomedialwall_dparc.label.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_desc-sulc_midthickness.shape.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_desc-vaavg_midthickness.shape.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_inflated.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_midthickness.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_sphere.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_den-32k_hemi-R_veryinflated.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_space-fsaverage_den-32k_hemi-L_sphere.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/human_fsLR/tpl-fsLR_space-fsaverage_den-32k_hemi-R_sphere.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.L.inflated.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.L.midthickness.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.L.pial.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.L.veryinflated.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.L.white.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.R.inflated.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.R.midthickness.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.R.pial.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.R.veryinflated.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_BNA/civm.R.white.32k_fs_LR.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/L.gray_surface.inf_300.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/L.gray_surface.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/L.mid_surface.inf_300.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/L.mid_surface.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/L.white_surface.inf_300.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/L.white_surface.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/R.gray_surface.inf_300.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/R.gray_surface.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/R.mid_surface.inf_300.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/R.mid_surface.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/R.white_surface.inf_300.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/surfaces/macaque_NMT2/R.white_surface.surf.gii +0 -0
- {plotfig-1.5.0 → plotfig-1.6.0}/src/plotfig/data/neurodata/volumes/macaque_NMT2/CHARM5_add_13_sgms_asym.nii.gz +0 -0
|
@@ -56,7 +56,7 @@ jobs:
|
|
|
56
56
|
"model": "deepseek-chat",
|
|
57
57
|
"messages": [
|
|
58
58
|
{"role": "system", "content": "You are a helpful assistant"},
|
|
59
|
-
{"role": "user", "content": "
|
|
59
|
+
{"role": "user", "content": "一句中文总结以下更新内容,适合放在公告栏(不允许出现“`”等特殊符号):${{ steps.changelog.outputs.added }}"}
|
|
60
60
|
]
|
|
61
61
|
}' | jq -r '.choices[0].message.content')
|
|
62
62
|
echo "response<<EOF" >> $GITHUB_OUTPUT
|
|
@@ -0,0 +1 @@
|
|
|
1
|
+
{".":"1.6.0"}
|
|
@@ -0,0 +1,147 @@
|
|
|
1
|
+
# Changelog
|
|
2
|
+
|
|
3
|
+
## [1.6.0](https://github.com/RicardoRyn/plotfig/compare/v1.5.1...v1.6.0) (2025-09-06)
|
|
4
|
+
|
|
5
|
+
|
|
6
|
+
### Features ✨
|
|
7
|
+
|
|
8
|
+
* **circos:** Implement a new method for drawing circos plots ([ebf3352](https://github.com/RicardoRyn/plotfig/commit/ebf3352491566817fc6202c1a9323e9f6e8a323a))
|
|
9
|
+
* **utils:** Add several utility functions ([b59f2a4](https://github.com/RicardoRyn/plotfig/commit/b59f2a49a6683e8ce942f47a2adc2a79a94e6f84))
|
|
10
|
+
|
|
11
|
+
|
|
12
|
+
### Bug Fixes 🔧
|
|
13
|
+
|
|
14
|
+
* **bar:** fix bug causing multi_bar plot failure ([a797006](https://github.com/RicardoRyn/plotfig/commit/a797006ed7b0598f65ff14f29d1c4c0280b1d811))
|
|
15
|
+
* **connec:** Fix color bug caused by integer values ([b104c1f](https://github.com/RicardoRyn/plotfig/commit/b104c1f985c4aeaf1576c716fc1f0b7725774e26))
|
|
16
|
+
|
|
17
|
+
|
|
18
|
+
### Code Refactoring ♻️
|
|
19
|
+
|
|
20
|
+
* **circos:** Temporarily disable circos plot ([a96bb09](https://github.com/RicardoRyn/plotfig/commit/a96bb09cc799ce34785146f6bd855631ae1ad73a))
|
|
21
|
+
* **corr/matrix:** function now returns Axes object ([e47cada](https://github.com/RicardoRyn/plotfig/commit/e47cada18a411fe28f7dc8a6ef62dea00acd3888))
|
|
22
|
+
* **corr:** change default ax title font size in correlation plots to 12 ([5aab9fe](https://github.com/RicardoRyn/plotfig/commit/5aab9fe082f05894379c90b7e7a4a5a3a4739c49))
|
|
23
|
+
* **surface:** Deprecate old functions ([d90dc92](https://github.com/RicardoRyn/plotfig/commit/d90dc927731cd369d2ac1cc0939556b13d54158c))
|
|
24
|
+
|
|
25
|
+
## [1.5.1](https://github.com/RicardoRyn/plotfig/compare/v1.5.0...v1.5.1) (2025-08-11)
|
|
26
|
+
|
|
27
|
+
|
|
28
|
+
### Bug Fixes
|
|
29
|
+
|
|
30
|
+
* **connec:** fix issue with line_color display under color scale ([83d46d7](https://github.com/RicardoRyn/plotfig/commit/83d46d7031c49a455ab2648a92193ae5278750f4))
|
|
31
|
+
|
|
32
|
+
|
|
33
|
+
### Code Refactoring
|
|
34
|
+
|
|
35
|
+
* **bar:** Remove the legacy `plot_one_group_violin_figure_old` function ([6d1316d](https://github.com/RicardoRyn/plotfig/commit/6d1316d3050279f849d5c941ff6280c0ce419145))
|
|
36
|
+
|
|
37
|
+
## [1.5.0](https://github.com/RicardoRyn/plotfig/compare/v1.4.0...v1.5.0) (2025-08-07)
|
|
38
|
+
|
|
39
|
+
|
|
40
|
+
### Features
|
|
41
|
+
|
|
42
|
+
* **bar:** support combining multiple statistical test methods ([34b6960](https://github.com/RicardoRyn/plotfig/commit/34b6960ff705468154bc5fbf75b9917ba8ac64fd))
|
|
43
|
+
* **connec:** Add `line_color` parameter to customize connection line colors ([e4de41e](https://github.com/RicardoRyn/plotfig/commit/e4de41effe495767cde0980ce5e2cee458d8b3a8))
|
|
44
|
+
|
|
45
|
+
|
|
46
|
+
### Code Refactoring
|
|
47
|
+
|
|
48
|
+
* **bar:** mark string input for `test_method` as planned for deprecation ([e56d6d7](https://github.com/RicardoRyn/plotfig/commit/e56d6d7b79104b6079619b73158e21ee284a5304))
|
|
49
|
+
|
|
50
|
+
## [1.4.0](https://github.com/RicardoRyn/plotfig/compare/v1.3.3...v1.4.0) (2025-07-30)
|
|
51
|
+
|
|
52
|
+
|
|
53
|
+
### Features
|
|
54
|
+
|
|
55
|
+
* **bar:** support color transparency adjustment via `color_alpha` argument ([530980d](https://github.com/RicardoRyn/plotfig/commit/530980dc346a338658d8333bb274004fcaac8d7d))
|
|
56
|
+
|
|
57
|
+
## [1.3.3](https://github.com/RicardoRyn/plotfig/compare/v1.3.2...v1.3.3) (2025-07-29)
|
|
58
|
+
|
|
59
|
+
|
|
60
|
+
### Bug Fixes
|
|
61
|
+
|
|
62
|
+
* **bar**: handle empty significance plot without error
|
|
63
|
+
|
|
64
|
+
## [1.3.2](https://github.com/RicardoRyn/plotfig/compare/v1.3.1...v1.3.2) (2025-07-29)
|
|
65
|
+
|
|
66
|
+
|
|
67
|
+
### Bug Fixes
|
|
68
|
+
|
|
69
|
+
* **deps**: use the correct version of surfplot
|
|
70
|
+
|
|
71
|
+
## [1.3.1](https://github.com/RicardoRyn/plotfig/compare/v1.3.0...v1.3.1) (2025-07-28)
|
|
72
|
+
|
|
73
|
+
|
|
74
|
+
### Bug Fixes
|
|
75
|
+
|
|
76
|
+
* **deps**: update surfplot dependency info to use GitHub version
|
|
77
|
+
|
|
78
|
+
## [1.3.0](https://github.com/RicardoRyn/plotfig/compare/v1.2.1...v1.3.0) (2025-07-28)
|
|
79
|
+
|
|
80
|
+
|
|
81
|
+
### Features
|
|
82
|
+
|
|
83
|
+
* **bar**: add one-sample t-test functionality
|
|
84
|
+
|
|
85
|
+
|
|
86
|
+
### Bug Fixes
|
|
87
|
+
|
|
88
|
+
* **bar**: isolate random number generator inside function
|
|
89
|
+
|
|
90
|
+
|
|
91
|
+
### Code Refactoring
|
|
92
|
+
|
|
93
|
+
* **surface**: unify brain surface plotting with new plot_brain_surface_figure
|
|
94
|
+
* **bar**: replace print with warnings.warn
|
|
95
|
+
* **bar**: rename arguments in plot_one_group_bar_figure
|
|
96
|
+
* **tests**: remove unused tests folder
|
|
97
|
+
|
|
98
|
+
## [1.2.1](https://github.com/RicardoRyn/plotfig/compare/v1.2.0...v1.2.1) (2025-07-24)
|
|
99
|
+
|
|
100
|
+
|
|
101
|
+
### Bug Fixes
|
|
102
|
+
|
|
103
|
+
* **bar**: rename `y_lim_range` to `y_lim` in `plot_one_group_bar_figure`
|
|
104
|
+
|
|
105
|
+
## [1.2.0](https://github.com/RicardoRyn/plotfig/compare/v1.1.0...v1.2.0) (2025-07-24)
|
|
106
|
+
|
|
107
|
+
|
|
108
|
+
### Features
|
|
109
|
+
|
|
110
|
+
* **violin**: add function to plot single-group violin fig
|
|
111
|
+
|
|
112
|
+
|
|
113
|
+
### Bug Fixes
|
|
114
|
+
|
|
115
|
+
* **matrix**: changed return value to None
|
|
116
|
+
|
|
117
|
+
## [1.1.0](https://github.com/RicardoRyn/plotfig/compare/v1.0.0...v1.1.0) (2025-07-21)
|
|
118
|
+
|
|
119
|
+
|
|
120
|
+
### Features
|
|
121
|
+
|
|
122
|
+
* **corr**: allow hexbin to show dense scatter points in correlation plot
|
|
123
|
+
* **bar**: support gradient color bars and now can change border color
|
|
124
|
+
|
|
125
|
+
## 1.0.0 (2025-07-03)
|
|
126
|
+
|
|
127
|
+
|
|
128
|
+
### Features
|
|
129
|
+
|
|
130
|
+
* **bar**: support plotting single-group bar charts with statistical tests
|
|
131
|
+
* **bar**: support plotting multi-group bars charts
|
|
132
|
+
* **corr**: support combined sactter and line correlation plots
|
|
133
|
+
* **matrix**: support plotting matrix plots (i.e. heatmaps)
|
|
134
|
+
* **surface**: support brain region plots for human, chimpanzee and macaque
|
|
135
|
+
* **circos**: support brain connectivity circos plots
|
|
136
|
+
* **connection**: support glass brain connectivity plots
|
|
137
|
+
|
|
138
|
+
|
|
139
|
+
### Bug Fixes
|
|
140
|
+
|
|
141
|
+
* **surface**: fix bug where function did not retrun fig only
|
|
142
|
+
* **surface**: fix bug where brain region with zero values were not displayed
|
|
143
|
+
|
|
144
|
+
|
|
145
|
+
### Code Refactoring
|
|
146
|
+
|
|
147
|
+
* **src**: refactor code for more readability and maintainability
|
|
@@ -1,63 +1,58 @@
|
|
|
1
1
|
Metadata-Version: 2.4
|
|
2
2
|
Name: plotfig
|
|
3
|
-
Version: 1.
|
|
3
|
+
Version: 1.6.0
|
|
4
4
|
Summary: Scientific plotting package for Cognitive neuroscience
|
|
5
5
|
Author-email: Ricardo Ryn <ricardoRyn1317@gmail.com>
|
|
6
6
|
License-File: LICENSE
|
|
7
7
|
Keywords: neuroscience,plotting,visualization
|
|
8
8
|
Requires-Python: >=3.11
|
|
9
|
-
Requires-Dist:
|
|
10
|
-
Requires-Dist:
|
|
9
|
+
Requires-Dist: kaleido>=1.0.0
|
|
10
|
+
Requires-Dist: loguru>=0.7.3
|
|
11
|
+
Requires-Dist: matplotlib>=3.10.6
|
|
11
12
|
Requires-Dist: nibabel>=5.3.2
|
|
12
|
-
Requires-Dist: numpy>=2.2
|
|
13
|
-
Requires-Dist:
|
|
14
|
-
Requires-Dist:
|
|
15
|
-
Requires-Dist: scipy>=1.
|
|
13
|
+
Requires-Dist: numpy>=2.3.2
|
|
14
|
+
Requires-Dist: plotly>=6.3.0
|
|
15
|
+
Requires-Dist: pycirclize>=1.10.0
|
|
16
|
+
Requires-Dist: scipy>=1.16.1
|
|
16
17
|
Requires-Dist: surfplot
|
|
18
|
+
Requires-Dist: tqdm>=4.67.1
|
|
17
19
|
Description-Content-Type: text/markdown
|
|
18
20
|
|
|
19
|
-
#
|
|
21
|
+
# plotfig
|
|
22
|
+
|
|
23
|
+
## 简介
|
|
20
24
|
|
|
21
25
|
`plotfig` 是一个专为科学数据可视化设计的 Python 库,致力于为认知神经科研工作人员提供高效、易用且美观的图形绘制工具。
|
|
22
|
-
该项目基于业界主流的可视化库—— `matplotlib`、`surfplot` 和 `plotly
|
|
26
|
+
该项目基于业界主流的可视化库—— `matplotlib`、`surfplot` 和 `plotly`等库开发,融合了三者的强大功能,能够满足神经科学、脑连接组学、相关性分析、矩阵可视化等多种科研场景下的复杂绘图需求。
|
|
23
27
|
|
|
24
28
|

|
|
25
29
|
|
|
26
|
-
|
|
27
|
-
## 项目结构
|
|
30
|
+
### 项目结构
|
|
28
31
|
|
|
29
32
|
项目采用模块化设计,核心代码位于 `src/plotfig/` 目录下,包含如下主要功能模块:
|
|
30
33
|
|
|
31
34
|
- `bar.py`:条形图绘制,适用于分组数据的对比展示。
|
|
32
35
|
- `correlation.py`:相关性矩阵可视化,便于分析变量间的相关性分布。
|
|
33
36
|
- `matrix.py`:通用矩阵可视化,支持多种配色和注释方式。
|
|
34
|
-
- `brain_surface.py
|
|
37
|
+
- `brain_surface.py`:脑表面可视化,实现三维脑表面图集结构的绘制。
|
|
38
|
+
- `circos.py`:弦图可视化,适合平面展示脑区之间的连接关系。
|
|
35
39
|
- `brain_connection.py`:玻璃脑连接可视化,支持复杂的脑网络结构展示。
|
|
36
|
-
- `circos.py`:环状图(Circos)绘制,适合平面展示脑区之间的连接关系。
|
|
37
|
-
|
|
38
40
|
|
|
39
|
-
|
|
41
|
+
### 文档与示例
|
|
40
42
|
|
|
41
43
|
`plotfig` 提供了网页文档和使用示例。具体参见[使用教程](https://ricardoryn.github.io/plotfig/)。
|
|
42
44
|
|
|
43
|
-
|
|
44
|
-
其模块化架构便于后续功能扩展和自定义开发。
|
|
45
|
-
结合 `matplotlib` 支持矢量图或高分辨率位图和交互式 HTML 输出,适合论文发表和学术展示。
|
|
46
|
-
|
|
47
|
-
# 安装
|
|
48
|
-
|
|
49
|
-
## 普通安装
|
|
45
|
+
## 安装
|
|
50
46
|
|
|
51
47
|
`plotfig` 支持通过 `pip` 或源码安装,要求 Python 3.11 及以上版本。
|
|
52
48
|
|
|
53
|
-
|
|
54
|
-
**使用 pip 安装 <small>(推荐)</small>**
|
|
49
|
+
### 使用 pip 安装 (推荐)
|
|
55
50
|
|
|
56
51
|
```bash
|
|
57
52
|
pip install plotfig
|
|
58
53
|
```
|
|
59
54
|
|
|
60
|
-
|
|
55
|
+
### 使用 GitHub 源码安装
|
|
61
56
|
|
|
62
57
|
```bash
|
|
63
58
|
git clone --depth 1 https://github.com/RicardoRyn/plotfig.git
|
|
@@ -65,53 +60,49 @@ cd plotfig
|
|
|
65
60
|
pip install .
|
|
66
61
|
```
|
|
67
62
|
|
|
68
|
-
|
|
63
|
+
### 依赖要求
|
|
69
64
|
|
|
70
|
-
`plotfig`
|
|
65
|
+
`plotfig` 依赖若干核心库,这些依赖将在安装过程中自动处理,但需要注意:
|
|
71
66
|
|
|
72
|
-
- [matplotlib](https://matplotlib.org/) ≥ 3.10.
|
|
73
|
-
- [mne-connectivity](https://mne.tools/mne-connectivity/stable/index.html) ≥ 0.7.
|
|
74
|
-
- [nibabel](https://nipy.org/nibabel/) ≥ 5.3.
|
|
75
|
-
- [numpy](https://numpy.org/) ≥ 2.2.4
|
|
76
|
-
- [pandas](https://pandas.pydata.org/) ≥ 2.2.
|
|
77
|
-
- [plotly](https://plotly.com/) ≥ 6.0.1
|
|
78
|
-
- [scipy](https://scipy.org/) ≥ 1.15.
|
|
79
67
|
- [surfplot](https://github.com/danjgale/surfplot) 需使用其 GitHub 仓库中的最新版,而非 PyPI 上的版本,因后者尚未包含所需功能。
|
|
80
68
|
|
|
81
69
|
> ⚠️ **指定 `surfplot` 版本**
|
|
82
70
|
>
|
|
83
|
-
> 由于 PyPI 上的 `surfplot` 版本较旧,缺少 `plotfig` 所需功能,建议通过以下步骤安装其 GitHub
|
|
84
|
-
>
|
|
85
|
-
> ```bash
|
|
86
|
-
> # 卸载旧版本
|
|
87
|
-
> pip uninstall surfplot
|
|
71
|
+
> 由于 PyPI 上的 `surfplot` 版本较旧,缺少 `plotfig` 所需功能,建议通过以下步骤安装其 GitHub 仓库的最新版。
|
|
88
72
|
>
|
|
89
|
-
>
|
|
90
|
-
> git clone --depth 1 https://github.com/danjgale/surfplot.git
|
|
91
|
-
> cd surfplot
|
|
92
|
-
> pip install .
|
|
93
|
-
>
|
|
94
|
-
> # 安装完成后,返回上级目录并删除源码文件夹
|
|
95
|
-
> cd ..
|
|
96
|
-
> rm -rf surfplot
|
|
97
|
-
> ```
|
|
73
|
+
> 如果您无须绘制 brain_surface 图,可以忽略此步骤。
|
|
98
74
|
|
|
99
|
-
|
|
75
|
+
```bash
|
|
76
|
+
# 卸载旧版本
|
|
77
|
+
pip uninstall surfplot
|
|
78
|
+
|
|
79
|
+
# 克隆源码并安装
|
|
80
|
+
git clone --depth 1 https://github.com/danjgale/surfplot.git
|
|
81
|
+
cd surfplot
|
|
82
|
+
pip install .
|
|
83
|
+
|
|
84
|
+
# 安装完成后,返回上级目录并删除源码文件夹
|
|
85
|
+
cd ..
|
|
86
|
+
rm -rf surfplot
|
|
87
|
+
```
|
|
100
88
|
|
|
101
|
-
|
|
89
|
+
## 贡献指南
|
|
102
90
|
|
|
91
|
+
如果您希望参与 `plotfig` 的开发,或者想体验尚未正式发布的新功能,可以选择以开发模式安装项目。
|
|
103
92
|
这种“可编辑模式(editable mode)”安装方式允许您对本地源码的修改立即生效,非常适合开发、调试和贡献代码。
|
|
104
93
|
|
|
105
94
|
推荐先 Fork 仓库,然后克隆您自己的 Fork:
|
|
106
95
|
|
|
107
96
|
```bash
|
|
108
|
-
git clone -b dev https://github.com/<your-username>/plotfig.git
|
|
97
|
+
git clone -b dev https://github.com/<your-username >/plotfig.git
|
|
109
98
|
cd plotfig
|
|
110
99
|
pip install -e .
|
|
111
100
|
```
|
|
112
101
|
|
|
113
102
|
**欢迎提交 Issue 或 PR!**
|
|
114
103
|
|
|
115
|
-
无论是 Bug
|
|
116
|
-
|
|
104
|
+
无论是 Bug 报告、功能建议、还是文档改进。
|
|
105
|
+
|
|
106
|
+
都非常欢迎在 [Issue](https://github.com/RicardoRyn/plotfig/issues) 中提出。
|
|
107
|
+
|
|
117
108
|
也可以直接提交 [PR](https://github.com/RicardoRyn/plotfig/pulls),一起变得更强 🙌!
|
|
@@ -1,45 +1,38 @@
|
|
|
1
|
-
#
|
|
1
|
+
# plotfig
|
|
2
|
+
|
|
3
|
+
## 简介
|
|
2
4
|
|
|
3
5
|
`plotfig` 是一个专为科学数据可视化设计的 Python 库,致力于为认知神经科研工作人员提供高效、易用且美观的图形绘制工具。
|
|
4
|
-
该项目基于业界主流的可视化库—— `matplotlib`、`surfplot` 和 `plotly
|
|
6
|
+
该项目基于业界主流的可视化库—— `matplotlib`、`surfplot` 和 `plotly`等库开发,融合了三者的强大功能,能够满足神经科学、脑连接组学、相关性分析、矩阵可视化等多种科研场景下的复杂绘图需求。
|
|
5
7
|
|
|
6
8
|

|
|
7
9
|
|
|
8
|
-
|
|
9
|
-
## 项目结构
|
|
10
|
+
### 项目结构
|
|
10
11
|
|
|
11
12
|
项目采用模块化设计,核心代码位于 `src/plotfig/` 目录下,包含如下主要功能模块:
|
|
12
13
|
|
|
13
14
|
- `bar.py`:条形图绘制,适用于分组数据的对比展示。
|
|
14
15
|
- `correlation.py`:相关性矩阵可视化,便于分析变量间的相关性分布。
|
|
15
16
|
- `matrix.py`:通用矩阵可视化,支持多种配色和注释方式。
|
|
16
|
-
- `brain_surface.py
|
|
17
|
+
- `brain_surface.py`:脑表面可视化,实现三维脑表面图集结构的绘制。
|
|
18
|
+
- `circos.py`:弦图可视化,适合平面展示脑区之间的连接关系。
|
|
17
19
|
- `brain_connection.py`:玻璃脑连接可视化,支持复杂的脑网络结构展示。
|
|
18
|
-
- `circos.py`:环状图(Circos)绘制,适合平面展示脑区之间的连接关系。
|
|
19
|
-
|
|
20
20
|
|
|
21
|
-
|
|
21
|
+
### 文档与示例
|
|
22
22
|
|
|
23
23
|
`plotfig` 提供了网页文档和使用示例。具体参见[使用教程](https://ricardoryn.github.io/plotfig/)。
|
|
24
24
|
|
|
25
|
-
|
|
26
|
-
其模块化架构便于后续功能扩展和自定义开发。
|
|
27
|
-
结合 `matplotlib` 支持矢量图或高分辨率位图和交互式 HTML 输出,适合论文发表和学术展示。
|
|
28
|
-
|
|
29
|
-
# 安装
|
|
30
|
-
|
|
31
|
-
## 普通安装
|
|
25
|
+
## 安装
|
|
32
26
|
|
|
33
27
|
`plotfig` 支持通过 `pip` 或源码安装,要求 Python 3.11 及以上版本。
|
|
34
28
|
|
|
35
|
-
|
|
36
|
-
**使用 pip 安装 <small>(推荐)</small>**
|
|
29
|
+
### 使用 pip 安装 (推荐)
|
|
37
30
|
|
|
38
31
|
```bash
|
|
39
32
|
pip install plotfig
|
|
40
33
|
```
|
|
41
34
|
|
|
42
|
-
|
|
35
|
+
### 使用 GitHub 源码安装
|
|
43
36
|
|
|
44
37
|
```bash
|
|
45
38
|
git clone --depth 1 https://github.com/RicardoRyn/plotfig.git
|
|
@@ -47,53 +40,49 @@ cd plotfig
|
|
|
47
40
|
pip install .
|
|
48
41
|
```
|
|
49
42
|
|
|
50
|
-
|
|
43
|
+
### 依赖要求
|
|
51
44
|
|
|
52
|
-
`plotfig`
|
|
45
|
+
`plotfig` 依赖若干核心库,这些依赖将在安装过程中自动处理,但需要注意:
|
|
53
46
|
|
|
54
|
-
- [matplotlib](https://matplotlib.org/) ≥ 3.10.
|
|
55
|
-
- [mne-connectivity](https://mne.tools/mne-connectivity/stable/index.html) ≥ 0.7.
|
|
56
|
-
- [nibabel](https://nipy.org/nibabel/) ≥ 5.3.
|
|
57
|
-
- [numpy](https://numpy.org/) ≥ 2.2.4
|
|
58
|
-
- [pandas](https://pandas.pydata.org/) ≥ 2.2.
|
|
59
|
-
- [plotly](https://plotly.com/) ≥ 6.0.1
|
|
60
|
-
- [scipy](https://scipy.org/) ≥ 1.15.
|
|
61
47
|
- [surfplot](https://github.com/danjgale/surfplot) 需使用其 GitHub 仓库中的最新版,而非 PyPI 上的版本,因后者尚未包含所需功能。
|
|
62
48
|
|
|
63
49
|
> ⚠️ **指定 `surfplot` 版本**
|
|
64
50
|
>
|
|
65
|
-
> 由于 PyPI 上的 `surfplot` 版本较旧,缺少 `plotfig` 所需功能,建议通过以下步骤安装其 GitHub
|
|
66
|
-
>
|
|
67
|
-
> ```bash
|
|
68
|
-
> # 卸载旧版本
|
|
69
|
-
> pip uninstall surfplot
|
|
51
|
+
> 由于 PyPI 上的 `surfplot` 版本较旧,缺少 `plotfig` 所需功能,建议通过以下步骤安装其 GitHub 仓库的最新版。
|
|
70
52
|
>
|
|
71
|
-
>
|
|
72
|
-
> git clone --depth 1 https://github.com/danjgale/surfplot.git
|
|
73
|
-
> cd surfplot
|
|
74
|
-
> pip install .
|
|
75
|
-
>
|
|
76
|
-
> # 安装完成后,返回上级目录并删除源码文件夹
|
|
77
|
-
> cd ..
|
|
78
|
-
> rm -rf surfplot
|
|
79
|
-
> ```
|
|
53
|
+
> 如果您无须绘制 brain_surface 图,可以忽略此步骤。
|
|
80
54
|
|
|
81
|
-
|
|
55
|
+
```bash
|
|
56
|
+
# 卸载旧版本
|
|
57
|
+
pip uninstall surfplot
|
|
58
|
+
|
|
59
|
+
# 克隆源码并安装
|
|
60
|
+
git clone --depth 1 https://github.com/danjgale/surfplot.git
|
|
61
|
+
cd surfplot
|
|
62
|
+
pip install .
|
|
63
|
+
|
|
64
|
+
# 安装完成后,返回上级目录并删除源码文件夹
|
|
65
|
+
cd ..
|
|
66
|
+
rm -rf surfplot
|
|
67
|
+
```
|
|
82
68
|
|
|
83
|
-
|
|
69
|
+
## 贡献指南
|
|
84
70
|
|
|
71
|
+
如果您希望参与 `plotfig` 的开发,或者想体验尚未正式发布的新功能,可以选择以开发模式安装项目。
|
|
85
72
|
这种“可编辑模式(editable mode)”安装方式允许您对本地源码的修改立即生效,非常适合开发、调试和贡献代码。
|
|
86
73
|
|
|
87
74
|
推荐先 Fork 仓库,然后克隆您自己的 Fork:
|
|
88
75
|
|
|
89
76
|
```bash
|
|
90
|
-
git clone -b dev https://github.com/<your-username>/plotfig.git
|
|
77
|
+
git clone -b dev https://github.com/<your-username >/plotfig.git
|
|
91
78
|
cd plotfig
|
|
92
79
|
pip install -e .
|
|
93
80
|
```
|
|
94
81
|
|
|
95
82
|
**欢迎提交 Issue 或 PR!**
|
|
96
83
|
|
|
97
|
-
无论是 Bug
|
|
98
|
-
|
|
84
|
+
无论是 Bug 报告、功能建议、还是文档改进。
|
|
85
|
+
|
|
86
|
+
都非常欢迎在 [Issue](https://github.com/RicardoRyn/plotfig/issues) 中提出。
|
|
87
|
+
|
|
99
88
|
也可以直接提交 [PR](https://github.com/RicardoRyn/plotfig/pulls),一起变得更强 🙌!
|
|
@@ -0,0 +1,20 @@
|
|
|
1
|
+
# API
|
|
2
|
+
|
|
3
|
+
::: plotfig.bar
|
|
4
|
+
options:
|
|
5
|
+
members:
|
|
6
|
+
- plot_one_group_bar_figure
|
|
7
|
+
- plot_one_group_violin_figure
|
|
8
|
+
- plot_multi_group_bar_figure
|
|
9
|
+
|
|
10
|
+
::: plotfig.correlation
|
|
11
|
+
|
|
12
|
+
::: plotfig.matrix
|
|
13
|
+
|
|
14
|
+
::: plotfig.brain_surface
|
|
15
|
+
|
|
16
|
+
::: plotfig.circos
|
|
17
|
+
|
|
18
|
+
::: plotfig.brain_connection
|
|
19
|
+
|
|
20
|
+
::: plotfig.utils
|
|
@@ -1,11 +1,10 @@
|
|
|
1
1
|
# 简介
|
|
2
2
|
|
|
3
3
|
`plotfig` 是一个专为科学数据可视化设计的 Python 库,致力于为认知神经科研工作人员提供高效、易用且美观的图形绘制工具。
|
|
4
|
-
该项目基于业界主流的可视化库—— `matplotlib`、`surfplot` 和 `plotly
|
|
4
|
+
该项目基于业界主流的可视化库—— `matplotlib`、`surfplot` 和 `plotly`等库开发,融合了三者的强大功能,能够满足神经科学、脑连接组学、相关性分析、矩阵可视化等多种科研场景下的复杂绘图需求。
|
|
5
5
|
|
|
6
6
|

|
|
7
7
|
|
|
8
|
-
|
|
9
8
|
## 项目结构
|
|
10
9
|
|
|
11
10
|
项目采用模块化设计,核心代码位于 `src/plotfig/` 目录下,包含如下主要功能模块:
|
|
@@ -13,12 +12,11 @@
|
|
|
13
12
|
- `bar.py`:条形图绘制,适用于分组数据的对比展示。
|
|
14
13
|
- `correlation.py`:相关性矩阵可视化,便于分析变量间的相关性分布。
|
|
15
14
|
- `matrix.py`:通用矩阵可视化,支持多种配色和注释方式。
|
|
16
|
-
- `brain_surface.py
|
|
15
|
+
- `brain_surface.py`:脑表面可视化,实现三维脑表面图集结构的绘制。
|
|
16
|
+
- `circos.py`:弦图可视化,适合平面展示脑区之间的连接关系。
|
|
17
17
|
- `brain_connection.py`:玻璃脑连接可视化,支持复杂的脑网络结构展示。
|
|
18
|
-
- `circos.py`:环状图(Circos)绘制,适合平面展示脑区之间的连接关系。
|
|
19
|
-
|
|
20
18
|
|
|
21
|
-
##
|
|
19
|
+
## 特性
|
|
22
20
|
|
|
23
21
|
`plotfig` API 设计简洁,参数灵活,适合科研人员和数据分析师快速集成到自己的数据分析流程中。
|
|
24
22
|
其模块化架构便于后续功能扩展和自定义开发。
|
|
@@ -29,5 +27,4 @@
|
|
|
29
27
|
烫知识:一张图上的所有元素[^1]。
|
|
30
28
|
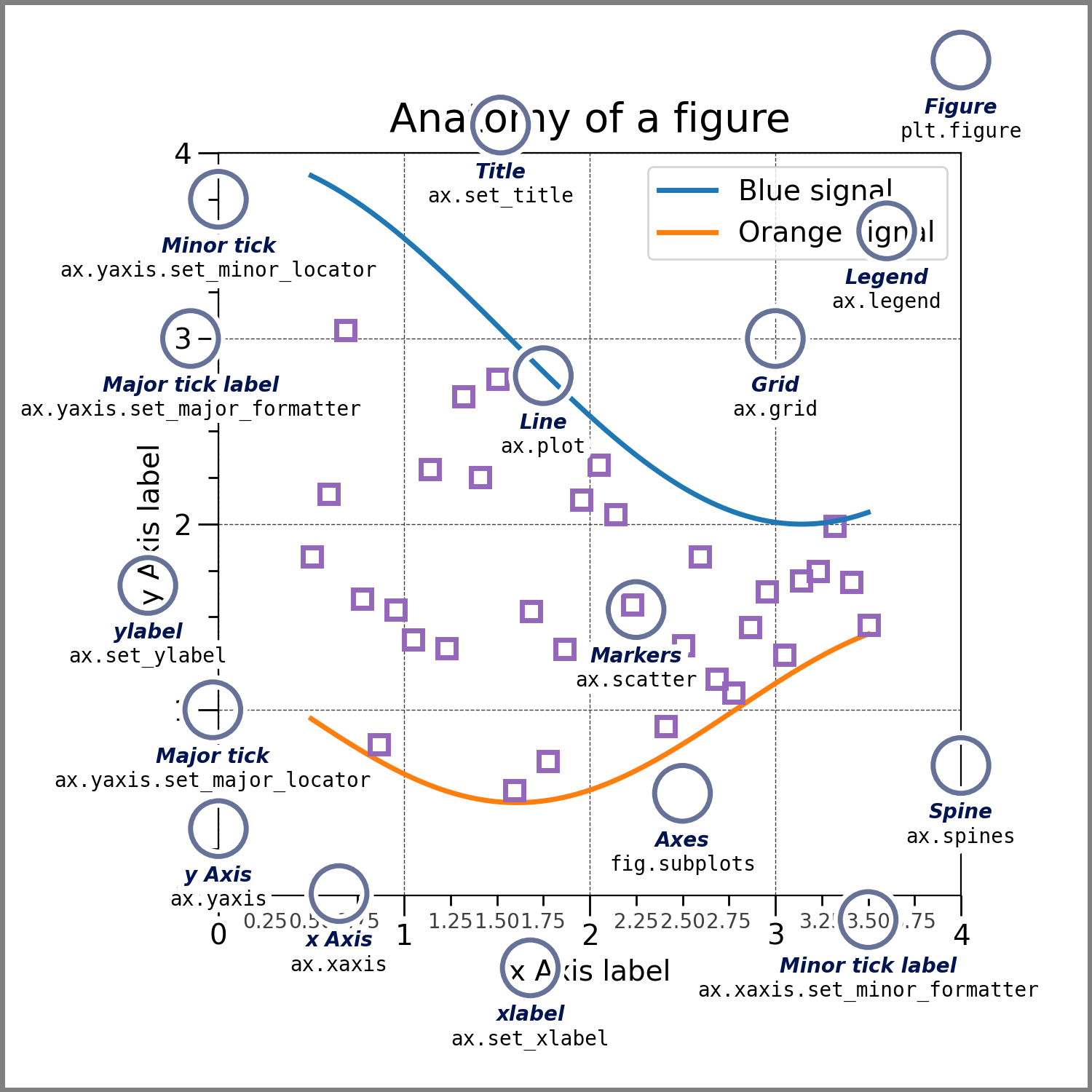
|
|
31
29
|
|
|
32
|
-
[^1]:
|
|
33
|
-
[Quick start guide of matplotlib.](https://matplotlib.org/stable/tutorials/introductory/usage.html#parts-of-a-figure)
|
|
30
|
+
[^1]: [Quick start guide of matplotlib.](https://matplotlib.org/stable/tutorials/introductory/usage.html#parts-of-a-figure)
|
|
@@ -4,13 +4,13 @@
|
|
|
4
4
|
|
|
5
5
|
`plotfig` 支持通过 `pip` 或源码安装,要求 Python 3.11 及以上版本。
|
|
6
6
|
|
|
7
|
-
|
|
7
|
+
### 使用 pip 安装 (推荐)
|
|
8
8
|
|
|
9
9
|
```bash
|
|
10
10
|
pip install plotfig
|
|
11
11
|
```
|
|
12
12
|
|
|
13
|
-
|
|
13
|
+
### 使用 GitHub 源码安装
|
|
14
14
|
|
|
15
15
|
```bash
|
|
16
16
|
git clone --depth 1 https://github.com/RicardoRyn/plotfig.git
|
|
@@ -20,20 +20,15 @@ pip install .
|
|
|
20
20
|
|
|
21
21
|
## 依赖要求
|
|
22
22
|
|
|
23
|
-
`plotfig`
|
|
23
|
+
`plotfig` 依赖若干核心库,这些依赖将在安装过程中自动处理,但需要注意:
|
|
24
24
|
|
|
25
|
-
- [matplotlib](https://matplotlib.org/) ≥ 3.10.1
|
|
26
|
-
- [mne-connectivity](https://mne.tools/mne-connectivity/stable/index.html) ≥ 0.7.0
|
|
27
|
-
- [nibabel](https://nipy.org/nibabel/) ≥ 5.3.2
|
|
28
|
-
- [numpy](https://numpy.org/) ≥ 2.2.4
|
|
29
|
-
- [pandas](https://pandas.pydata.org/) ≥ 2.2.3
|
|
30
|
-
- [plotly](https://plotly.com/) ≥ 6.0.1
|
|
31
|
-
- [scipy](https://scipy.org/) ≥ 1.15.2
|
|
32
25
|
- [surfplot](https://github.com/danjgale/surfplot) 需使用其 GitHub 仓库中的最新版,而非 PyPI 上的版本,因后者尚未包含所需功能。
|
|
33
26
|
|
|
34
27
|
!!! warning "指定 `surfplot` 版本"
|
|
35
28
|
|
|
36
|
-
由于 PyPI 上的 `surfplot` 版本较旧,缺少 `plotfig` 所需功能,建议通过以下步骤安装其 GitHub
|
|
29
|
+
由于 PyPI 上的 `surfplot` 版本较旧,缺少 `plotfig` 所需功能,建议通过以下步骤安装其 GitHub 仓库的最新版。
|
|
30
|
+
|
|
31
|
+
如果您无须绘制 brain_surface 图,可以忽略此步骤。
|
|
37
32
|
|
|
38
33
|
```bash
|
|
39
34
|
# 卸载旧版本
|
|
@@ -51,8 +46,7 @@ pip install .
|
|
|
51
46
|
|
|
52
47
|
## 贡献指南
|
|
53
48
|
|
|
54
|
-
如果您希望参与 `plotfig`
|
|
55
|
-
|
|
49
|
+
如果您希望参与 `plotfig` 的开发,或者想体验尚未正式发布的新功能,可以选择以开发模式安装项目。
|
|
56
50
|
这种“可编辑模式(editable mode)”安装方式允许您对本地源码的修改立即生效,非常适合开发、调试和贡献代码。
|
|
57
51
|
|
|
58
52
|
推荐先 Fork 仓库,然后克隆您自己的 Fork:
|
|
@@ -65,6 +59,8 @@ pip install -e .
|
|
|
65
59
|
|
|
66
60
|
**欢迎提交 Issue 或 PR!**
|
|
67
61
|
|
|
68
|
-
无论是 Bug
|
|
69
|
-
|
|
62
|
+
无论是 Bug 报告、功能建议、还是文档改进。
|
|
63
|
+
|
|
64
|
+
都非常欢迎在 [Issue](https://github.com/RicardoRyn/plotfig/issues) 中提出。
|
|
65
|
+
|
|
70
66
|
也可以直接提交 [PR](https://github.com/RicardoRyn/plotfig/pulls),一起变得更强 🙌!
|
|
Binary file
|
|
Binary file
|
|
Binary file
|